Author: Cynthia SC (05-14-2026)
⏱️ Tiempo de lectura aproximado: 10 min
Cell Calling en scRNA-seq
Por qué un barcode “no” siempre representa una célula real
Contenido
- Una idea peligrosa sobre scRNA-seq
- Entonces… ¿qué es realmente un barcode?
- ¿Qué significa droplet-based?
- Cell Ranger ya realiza cell calling
- EmptyDrops y el modelado de RNA ambiental
- No todas las tecnologías generan droplets
- Herramientas especializadas para tecnologías droplet-based
- Relación conceptual con Seurat
- Aprender single-cell más allá de los pipelines
Una idea peligrosa sobre scRNA-seq
Uno de los errores más frecuentes al comenzar en análisis single-cell RNA-seq es asumir que:
1 barcode = 1 célula
En realidad, esto no siempre es cierto.
En tecnologías droplet-based como 10x Genomics, el experimento genera millones de droplets, pero muchos de ellos:
- están vacíos
- contienen RNA ambiental
- contienen múltiples células (doublets)
- o presentan señales ambiguas
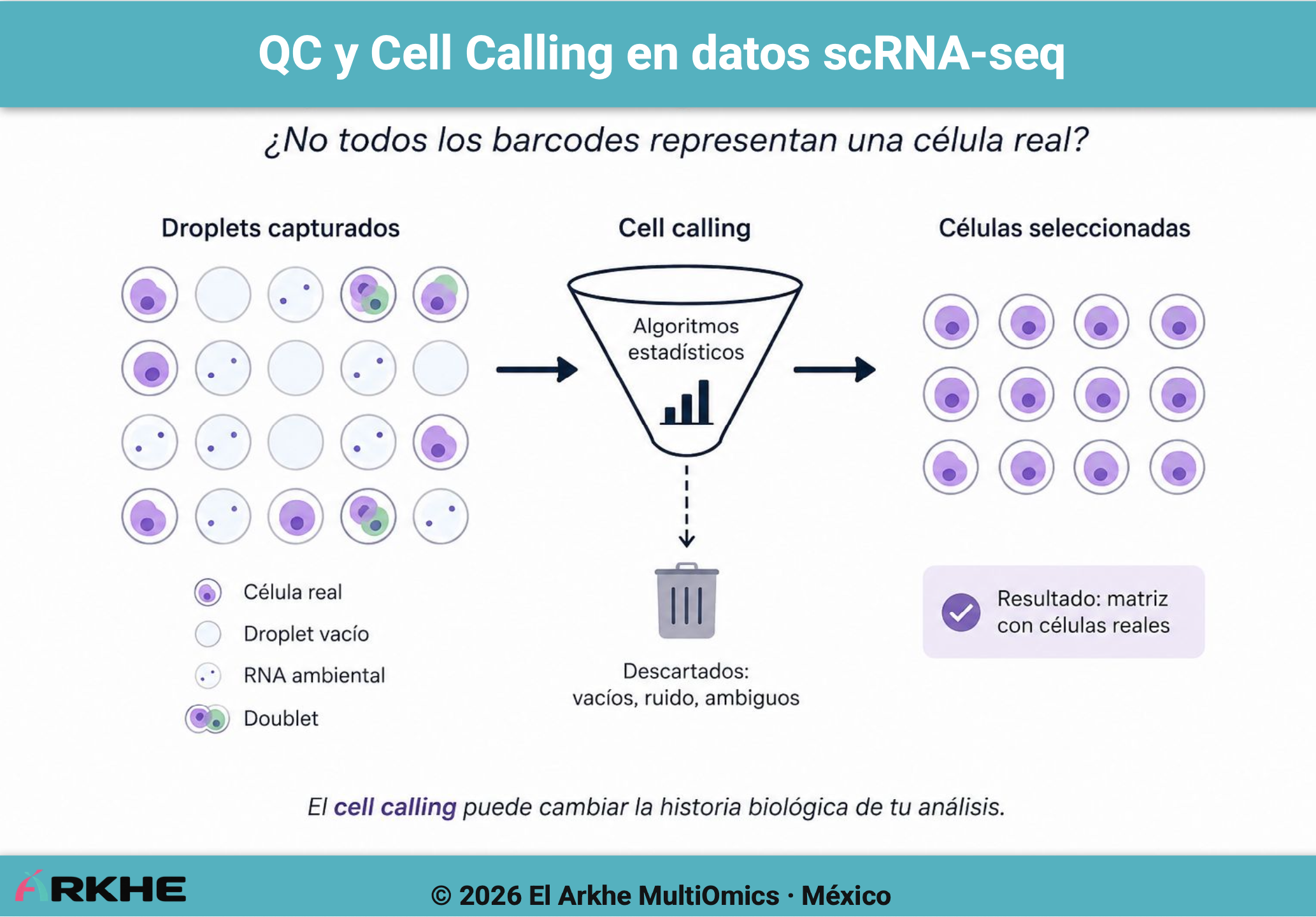
Por ello, antes del análisis biológico, existe una etapa crítica llamada cell calling
es decir:
decidir qué barcodes representan células reales y cuáles NO.
Entonces… ¿qué es realmente un barcode?
En tecnologías droplet-based, cada droplet recibe un identificador molecular conocido como cell barcode. Este barcode permite asociar lecturas de secuenciación a un droplet específico.
El detalle importante es que:
un barcode identifica un droplet, NO necesariamente una célula.
Por ello, una matriz raw típica puede contener:
1,000,000+ barcodes
aunque solamente una fracción corresponde a células reales.
¿Qué significa droplet-based?
Las tecnologías droplet-based buscan encapsular células individuales dentro de gotas microscópicas (droplets) utilizando sistemas microfluídicos.
Idealmente se quiere una equivalencia, 1 droplet → 1 célula
Sin embargo, la realidad experimental es mucho más compleja y cada droplet contiene:
- una célula (idealmente), no siempre es así
- reactivos de retrotranscripción
- un barcode celular
- UMIs (Unique Molecular Identifiers)
El problema: es que “no” todos los droplets contienen células
En la práctica, un experimento droplet-based genera una mezcla de droplets vacíos, droplets con una célula, droplets con múltiples células (doublets/multiplets) y droplets contaminados con RNA ambiental libre (ambient RNA).
Por ello, los datos sin procesar contienen millones de barcodes cuya composición real no se conoce inicialmente.
Por ejemplo, una matriz raw_feature_bc_matrix.h5 típica puede contener:
1,389,510 droplets × 38,606 genes
aunque la mayoría de esos droplets están vacíos.
Cuando observamos matrices sin filtrar, en realidad estamos viendo una mezcla compleja de señales biológicas y técnicas, que pueden resumirse como sigue:
| Problema | Descripción |
|---|---|
| Empty droplets | Barcodes sin células reales |
| Ambient RNA | RNA libre capturado accidentalmente |
| Doublets | Dos o más células encapsuladas juntas |
| Barcode contamination | Señales espurias entre droplets |
En este contexto, el cell calling intenta reconstruir correctamente qué señales corresponden a biología real.
Cell Ranger ya realiza cell calling
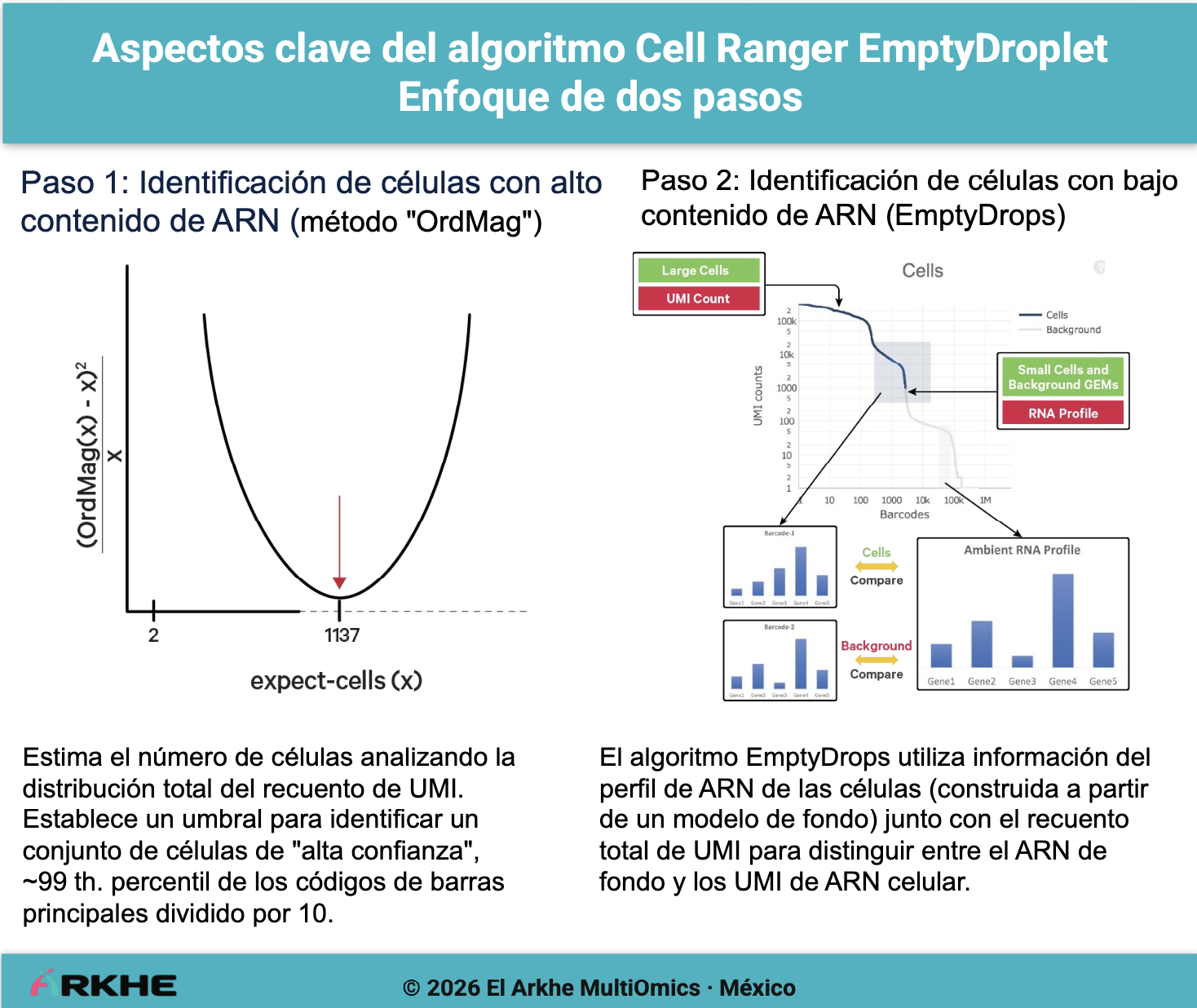
Cell Ranger implementa algoritmos estadísticos para decidir qué droplets contienen células reales. De forma simplificada sigue el siguiente flujo:
raw matrix
↓
estimación de RNA ambiental
↓
detección estadística de droplets celulares
↓
filtered matrix
Se describen resumidamente en la siguiente figura:
Es decir, despues del cell calling, Cell Ranger genera una matriz filtrada (filtered_feature_bc_matrix.h5) que contiene únicamente los barcodes que se consideran células reales:
Por ello muchos usuarios la utilizan directamente:
filtered_feature_bc_matrix
Aunque… algunas veces convendrá preguntarse:
- ¿cómo fueron seleccionados esos barcodes?
- ¿qué criterios utilizó Cell Ranger?
- ¿qué barcodes quedaron fuera?
- ¿qué impacto tiene esto en downstream analysis?
esto, será particularmente relevante en experimentos con datos de alta complejidad.
Y aquí, una pregunta importante
¿Debemos aceptar siempre los barcodes seleccionados automáticamente?
La respuesta corta es, “depende del experimento”
En algunos datasets:
- Cell Ranger puede ser demasiado conservador
- células raras pueden perderse
- poblaciones de baja expresión pueden desaparecer
- o el RNA ambiental puede afectar la selección
Por ello, muchos análisis avanzados exploran también la matriz raw.
EmptyDrops y el modelado de RNA ambiental
Una de las herramientas más conocidas para este problema es EmptyDrops, propuesta por Lun et al. (2019).
Aquí, la idea conceptual:
- comparar cada barcode contra el perfil de RNA ambiental esperado.
- Si el barcode presenta una señal significativamente distinta del ambiente, probablemente contiene una célula real.
Esto permite detectar:
- células de baja expresión
- poblaciones raras
- droplets ambiguos
- señales que podrían perderse en filtros automáticos
¿Puede estó cambiar un análisis?
La selección de barcodes puede modificar:
- número total de células
- composición celular
- detección de poblaciones raras
- clustering
- análisis diferencial
- interpretación biológica
En otras palabras:
el cell calling puede cambiar completamente la historia biológica que observamos.
Y este es uno de los motivos por los cuales esta etapa es mucho más importante de lo que muchos tutoriales sugieren.
No todas las tecnologías generan droplets
Es importante recordar que no todas las plataformas de scRNA-seq utilizan droplets.
Existen múltiples arquitecturas experimentales y cada una produce datos con propiedades distintas.
| Tipo de tecnología | Ejemplo |
|---|---|
| Droplet-based | 10x Genomics, Drop-seq, inDrop |
| Plate-based | Smart-seq2 |
| Microwell-based | Seq-Well |
Esto es importante porque muchas herramientas modernas fueron diseñadas específicamente para tecnologías droplet-based.
Ejemplo: Smart-seq2
Las tecnologías plate-based funcionan de manera distinta. Por ejemplo, en Smart-seq2:
- cada célula se deposita individualmente en un pozo
- no existen millones de droplets vacíos
- el RNA ambiental tiene un comportamiento distinto
- no se requiere cell calling
Por ello, herramientas como EmptyDrops no tienen sentido en estos datasets.
Herramientas especializadas para tecnologías droplet-based
Muchas herramientas modernas de scRNA-seq fueron desarrolladas específicamente para resolver problemas característicos de tecnologías droplet-based.
| Problema | Herramienta típica | ¿Qué hace? |
|---|---|---|
| Droplets vacíos | EmptyDrops / Cell Ranger | Identifica droplets con células reales |
| RNA ambiental | SoupX | Corrige contaminación por RNA ambiental |
| Doublets | scDblFinder | Detecta múltiples células en un mismo droplet |
Estas herramientas NO son universales, y dependen fuertemente del tipo de tecnología utilizada.
Comprender la arquitectura experimental evita aplicar herramientas incorrectas simplemente porque aparecen en un tutorial o pipeline popular.
Relación conceptual con Seurat
Es importante enfatizar que Seurat es una plataforma de análisis downstream y no reemplaza las etapas iniciales de preprocesamiento experimental.
El flujo conceptual correcto es:
FASTQ
↓
alignment / counting
↓
cell calling
↓
normalización
↓
clustering
↓
análisis downstream
Por ello:
EmptyDropspertenece a la fase de cell calling- Seurat comienza típicamente después de esta etapa
Lo importante no es memorizar herramientas
La verdadera pregunta en scRNA-seq no es:
“¿Qué comando debo correr?”
Sino:
“¿Qué representa realmente este barcode?”
Comprender esto cambia completamente la forma de analizar datos single-cell.
Aprender single-cell más allá de los pipelines
Gran parte de los tutoriales modernos muestran únicamente:
Read10X()
→ CreateSeuratObject()
→ NormalizeData()
→ RunUMAP()
Pero rara vez explican:
- qué ocurrió antes
- cómo fueron seleccionadas las células
- qué decisiones estadísticas tomó el pipeline
- o qué sesgos podrían introducirse
Comprender estas etapas mejora enormemente la interpretación biológica y evita aplicar herramientas como si fueran universales.
Recursos de consulta
© 2026 El Arkhe MultiOmics · México
